Խ��Խ����о�����������ܶ༲���볦������������еĹ�ϵ������������ij�̶ֳ��Ͽ��Է�ӳ����״̬��Ҳ��ˣ�Խ��Խ����о���ʼӦ�ó������ﹹ�����ģ�͡����������������ģ�ʹ���һ���ϴ���ϰ� - ����ЧӦ����һ������ѵ���õ���ģ����Ӧ����������������Ⱥ����������Ⱥ��������ĵ�����������ɵġ�
������ܵ���ƪ�·�������Gut�������£������пƼ���ѧ���������Ŷ�������֮ǰ������Ǩ��ѧϰ��ܣ�EXPERT����Ӧ���ڿ˷���������Ŀ�������ϵ�����ЧӦ�ϡ�����֮ǰ�Ĺ��ں������жԸ�Ǩ��ѧϰ�����������ܣ��÷����ѷ�����Brief in Bioinformatics����
BioRxiv | EXPERT������Ǩ��ѧϰ����������Դ��
Ǩ��ѧϰ���ԡ����á�Դ���еij��켲��֪ʶ������Ŀ����еļ���������ر�����Ŀ����е�����Ⱥģʽ֪ʶ���ٵ�����¡�
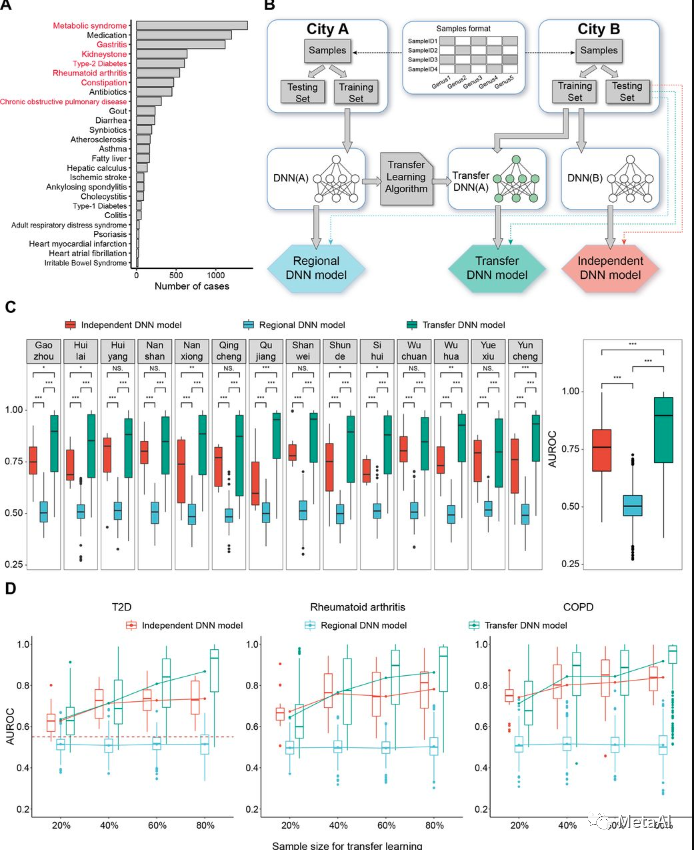
ͼ1. ���ݷָ�����������̺Ϳ������
Ϊ������������ܣ��о���Ա�ӹ㶫����������ƻ��л���������������ݡ���Щ��������14�����У�ѡ����7���д����Եļ�������������ͼ1A������ÿ�����е����������Ϊѵ���Ӽ��Ͳ����Ӽ���Ĭ��Ϊ80%��20%����Ȼ�������ģ�ͽ�����������1���������������磨DNN��ģ�ͣ��ֱ��ÿ�����е�ѵ���Ӽ��Ͳ����Ӽ����д�ͷѵ���Ͳ���DNNģ�͡�(2) ����DNNģ�ͣ�ʹ��һ������A��Դ���У���ѵ���Ӽ���DNNģ�ͽ��г�ʼѵ����������һ������B��Ŀ����У��IJ����Ӽ��н��в��ԡ�(3) Ǩ��DNNģ�ͣ�ʹ��һ������A��ѵ���Ӽ���ѵ��DNNģ�ͣ�Ȼ��Գ���B��һ����������20%��80%��������Ӧ��Ǩ��ѧϰ��Ȼ���ڳ���B�IJ����Ӽ��ϲ���Ǩ��DNNģ�ͣ�ͼ1B����
������֣�����е�����DNNģ�ͳ��ֳ�0.506�ĵ�ƽ�����ȣ�������DNNģ�͵�ƽ������Ϊ0.743��ͼ1C������������������ںܴ�̶��������˿�������ϣ���ǰ���о�Ҳ��������һ�㡣Ȼ����Ǩ��DNNģ����̵�����˿���е�Ԥ��ȷ�ԣ�ƽ��ȷ��Ϊ0.829��ͼ1C������Ȥ���ǣ�һ��Ŀ�����ʹ�õ�������������50%��Ǩ��DNNģ���������Գ��ֳ��ȶ���DNNģ���ߵ�Ԥ�⾫�ȣ�ͼ1D�������⣬�������ַ���Ӧ���������ʶ���ʱ��Ǩ��DNNģ��Ҳ�����õı��֡�
���⣬��������Ļ���ѧϰ�����ʶ�������ض��������Լ����������������﷽������������� ��leave-one-feature-out�����ķ���������ijЩ�ܵ���Ӱ��ϴ�������Enterobacteriaceae��Clostridium�������������ܵ���Ӱ���С����Parabacteroides��Faecalibacterium�������Ʋ⣬�����ض����������������Ǩ��DNNģ���ڿ�������ϼ����������Ч�ԡ�
��֮�������о�������ͨ�����ÿ��������������֪ʶ��Ǩ��ѧϰ����ʵ�ֻ�������Ŀ�������ϣ������нϸߵ�ȷ�Ժ��Ƚ����������о��ṩ��һ���µij��������Գ�Խ�������ƣ�ͨ���˹����ܼ����ٽ��ٴ������л�������Ŀ�������ϡ�
���룺https://github.com/HUST-NingKang-Lab/EXPERT-Disease-GGMP
Wang N, Cheng M, Ning K.Overcoming regional limitations: transfer learning for cross-regional microbial-based diagnosis of diseases. Gut Published Online First: 28 October 2022. doi: 10.1136/gutjnl-2022-328216 |